5+5[1] 1025/5[1] 52*2[1] 427-2[1] 25Metodología Cuantitativa Avanzada - Magíster en Ciencias Sociales
21 de marzo de 2025
Esta práctica tiene dos objetivos:
Generar un primer acercamiento al uso de R y Rstudio, conociendo su interfaz y sus principales funcionalidades y
Revisar algunos procedimientos básicos de la preparación de datos con R, que son necesarios para luego poder aplicar los contenidos más específicos de este curso.
Se encuentra un guía detallada para la instalación de R y RStudio en la descripción de los prácticos.
En primer lugar vamos a abrir un archivo de R (script). Esto se puede hacer manualmente con File -> new file -> R script o directamente con ctrl + shift + N.
Esta es nuestra hoja de código, que utilizaremos para procesar bases de datos, modificar variables y crear tablas y gráficos.
Uno de los usos más sencillos y que están a la base de R, es usarlo como una calculadora.
Como podrás ver, el resultado de estas instrucciones aparecen como un [1] en la consola. También podemos hacer operatorias más complejas y con más cálculos.
Se pueden crear objetos y asignarles valores
O asignar operaciones a un objeto
Así como también agregar texto
Y operaciones un poco más complejas
Sin embargo, la mayor parte del tiempo usamos funciones que ya existen en R
Tal vez una de las dificultades más comunes o cotidianas del uso de R es el orden de trabajo, en donde tenemos cientos de archivos, scripts, gráficos, bases de datos u otros repartidos desordenadamente en nuestro computador. También se da mucho el caso en que, cuando queremos trabajar con alguien, tenemos que cambiar las rutas de los archivos, por ejemplo en dónde están las bases de datos, ya que nuestros ordenadores y usuarios se llaman y son escencialmente distintos.
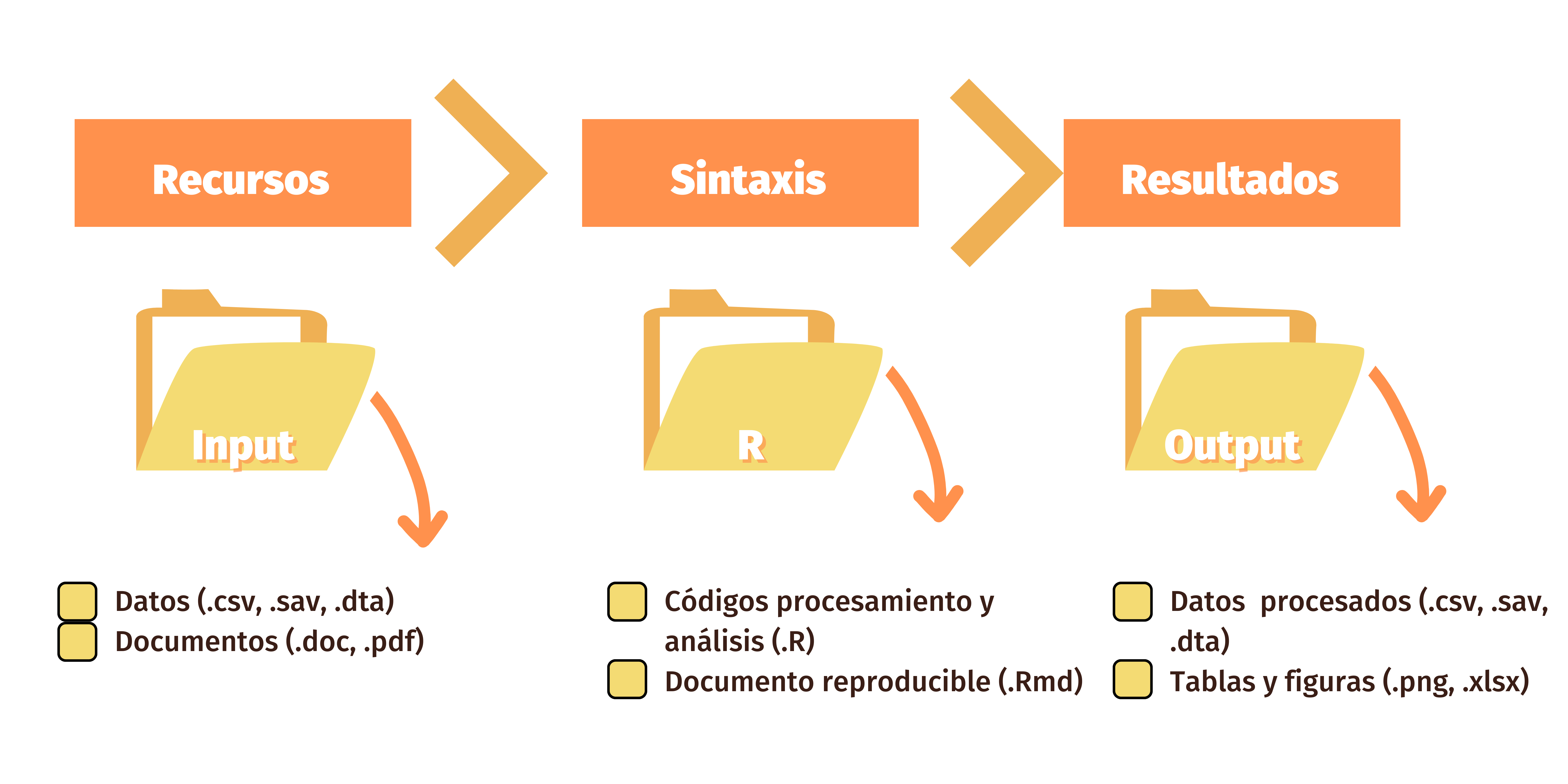
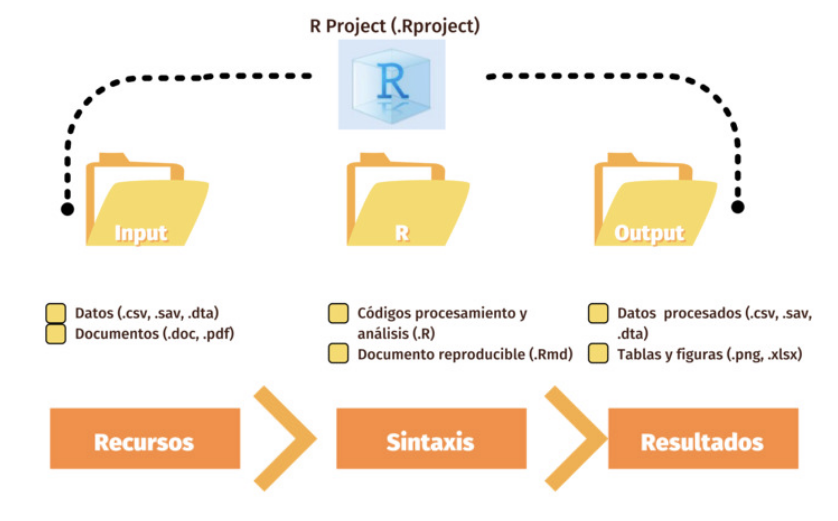
¿Cómo podemos sortear eso? Como se mencionó de manera introductoria en el práctico 01, lo podemos hacer siguiendo un flujo de trabajo reproducible, autocontenido y ordenado. En este curso trabajaremos R con un flujo de trabajo reproducible, basado en el sistema IPO. El protocolo IPO es una plantilla/protocolo de estructura digital de carpetas que tiene por objetivo el organizar, procesar y documentar los datos de un proyecto de investigación con miras a la apertura de los datos en un repositorio público y de acceso libre. En concreto, el sistema IPO se propone abordar brevemente todo lo referente a los Datos, Métodos y Resultados.
Lleva este nombre por el sistema de carpetas que se implementan: Input, Procesamiento y Output. En la carpeta Input guardaremos todos aquellso recursos iniciales que usaremos, como las bases de datos, el libro de códigos, entre otros. En la carpeta de Procesamiento, como dice el nombre, guardaremos todos los archivos que procesen y analicen datos. En la carpeta Output guardaremos todo aquello que hayamos producido en los archivos de procesamiento, como las bases de datos procesadas listas para compartir o publicas, los documentos de reporte, informes o analísis, gráficos o tablas.
 La implementación de la reproducibilidad en este tipo de protocolos se basa en generar un conjunto de archivos auto-contenidos organizado en una estructura de proyecto que cualquier persona pueda compartir y ejecutar. En otras palabras, debe tener todo lo que necesita para ejecutar y volver a ejecutar el análisis. Para conocer más, visita el Laboratorio de Ciencia Abierta.
La implementación de la reproducibilidad en este tipo de protocolos se basa en generar un conjunto de archivos auto-contenidos organizado en una estructura de proyecto que cualquier persona pueda compartir y ejecutar. En otras palabras, debe tener todo lo que necesita para ejecutar y volver a ejecutar el análisis. Para conocer más, visita el Laboratorio de Ciencia Abierta.
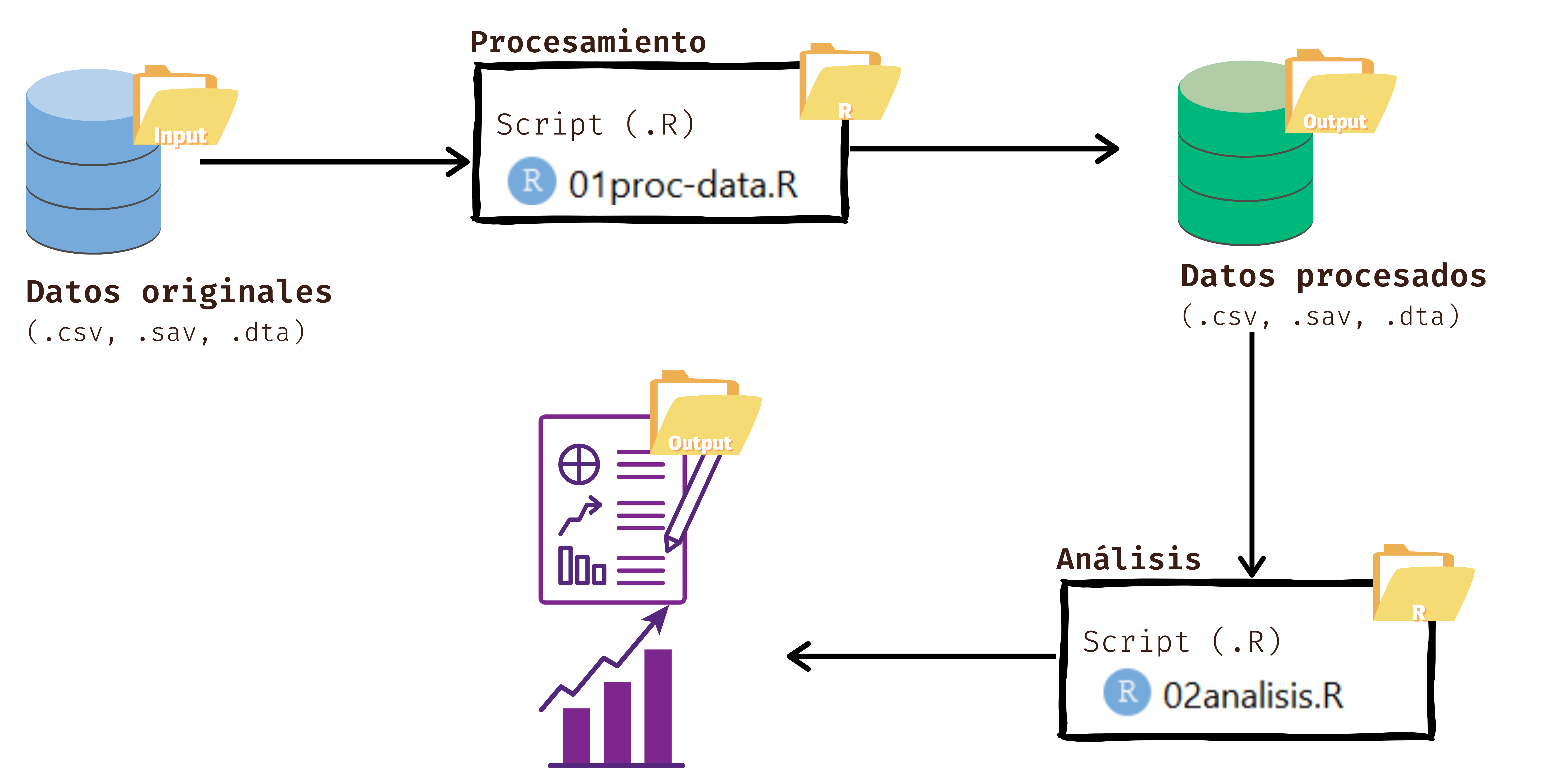
Un Rproject es una herramienta de R que nos permite establecer un directorio de trabajo en una carpeta de nuestro computador. Al hacerlo, establecemos un espacio de trabajo que permite crear una estructura de carpetas donde guardar los documentos asociados al proyecto. De esta forma, creamos un conjunto de archivos autocontenidos en un solo lugar que nos permite organizar nuestro trabajo y facilitar la reproducibilidad. En las próximas sesiones estableceremos un protocolo de trabajo que permite organizar y armonizar el trabajo: el protocolo IPO.
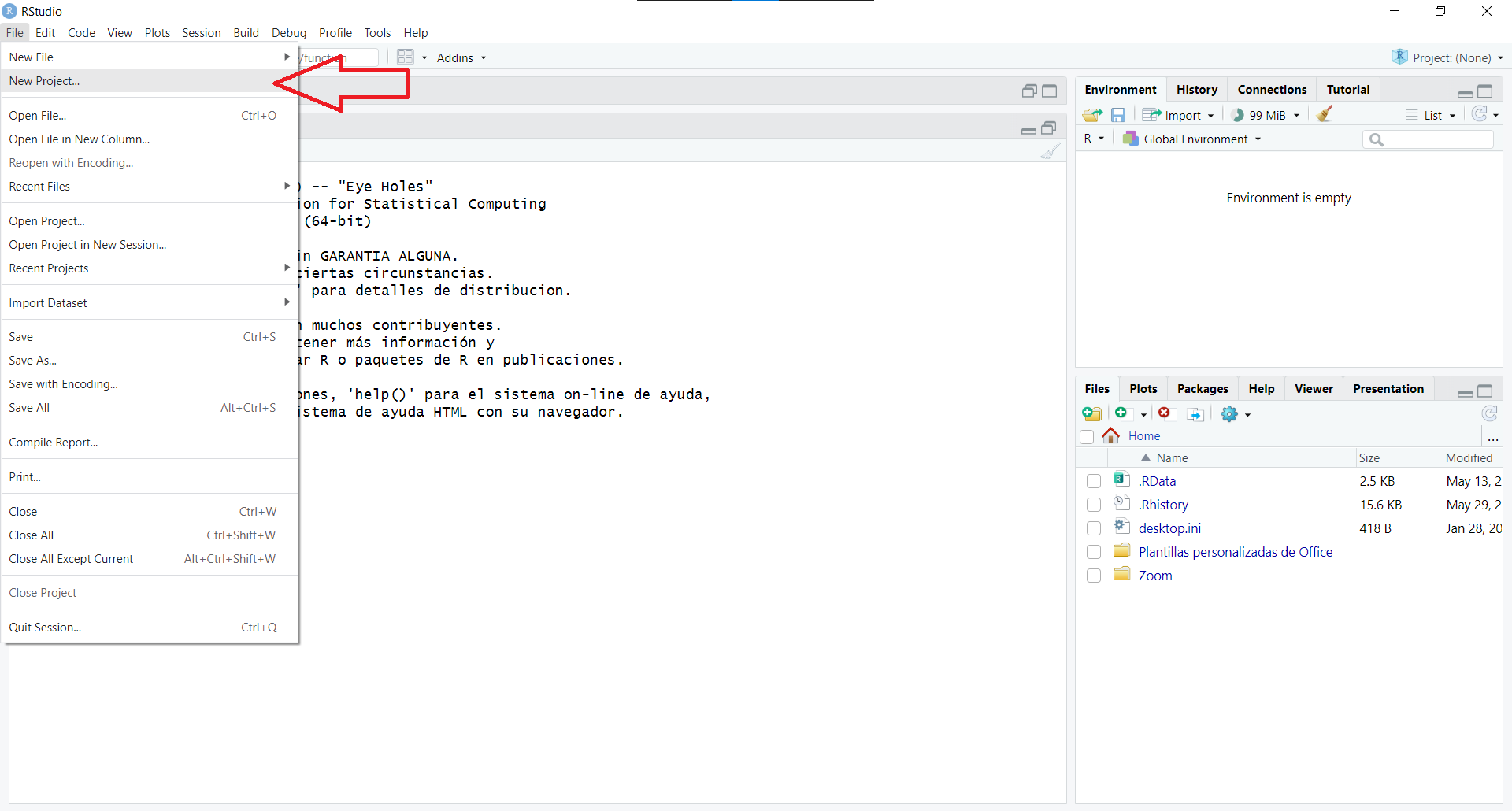
Abrir Rstudio
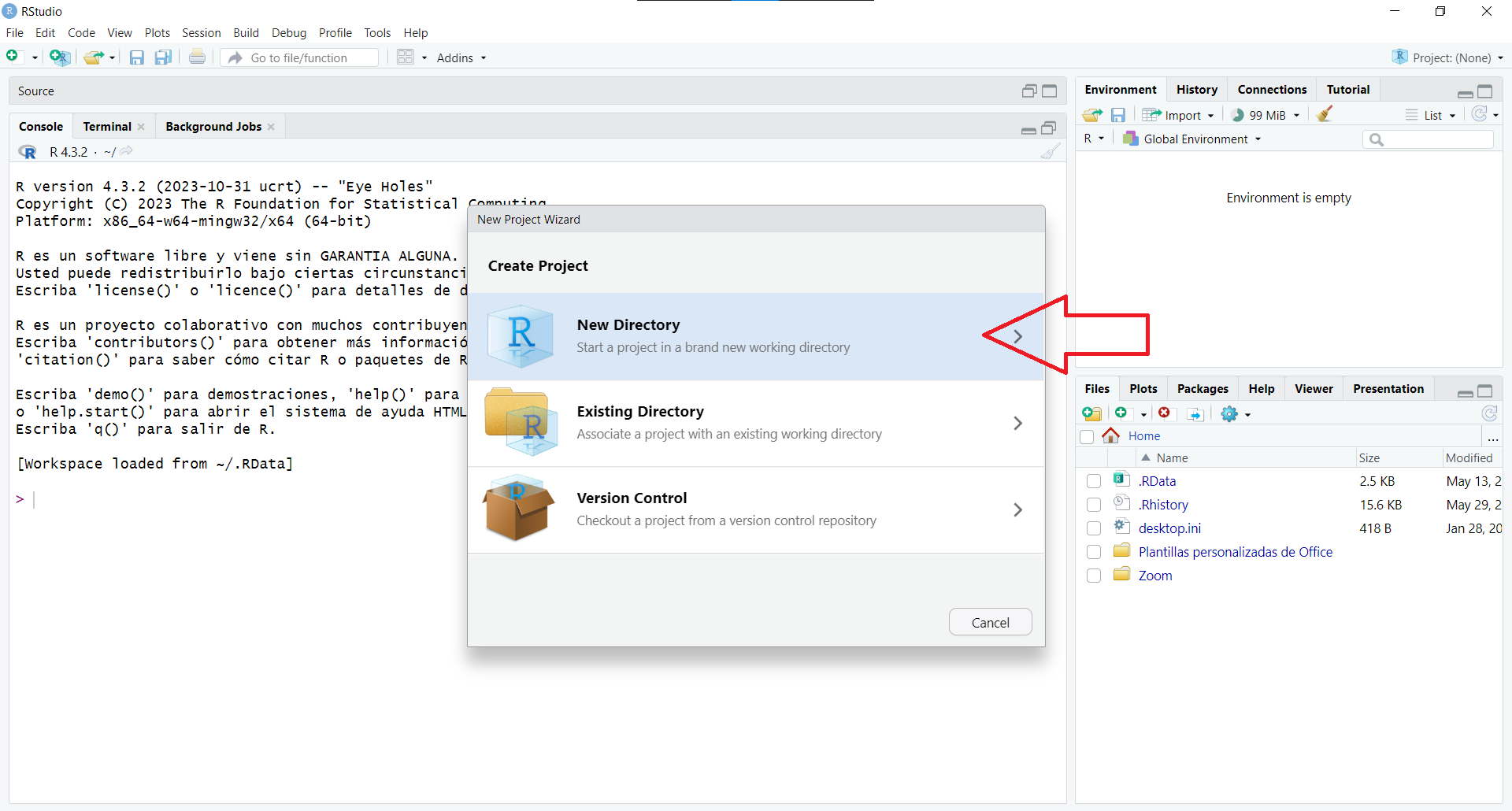
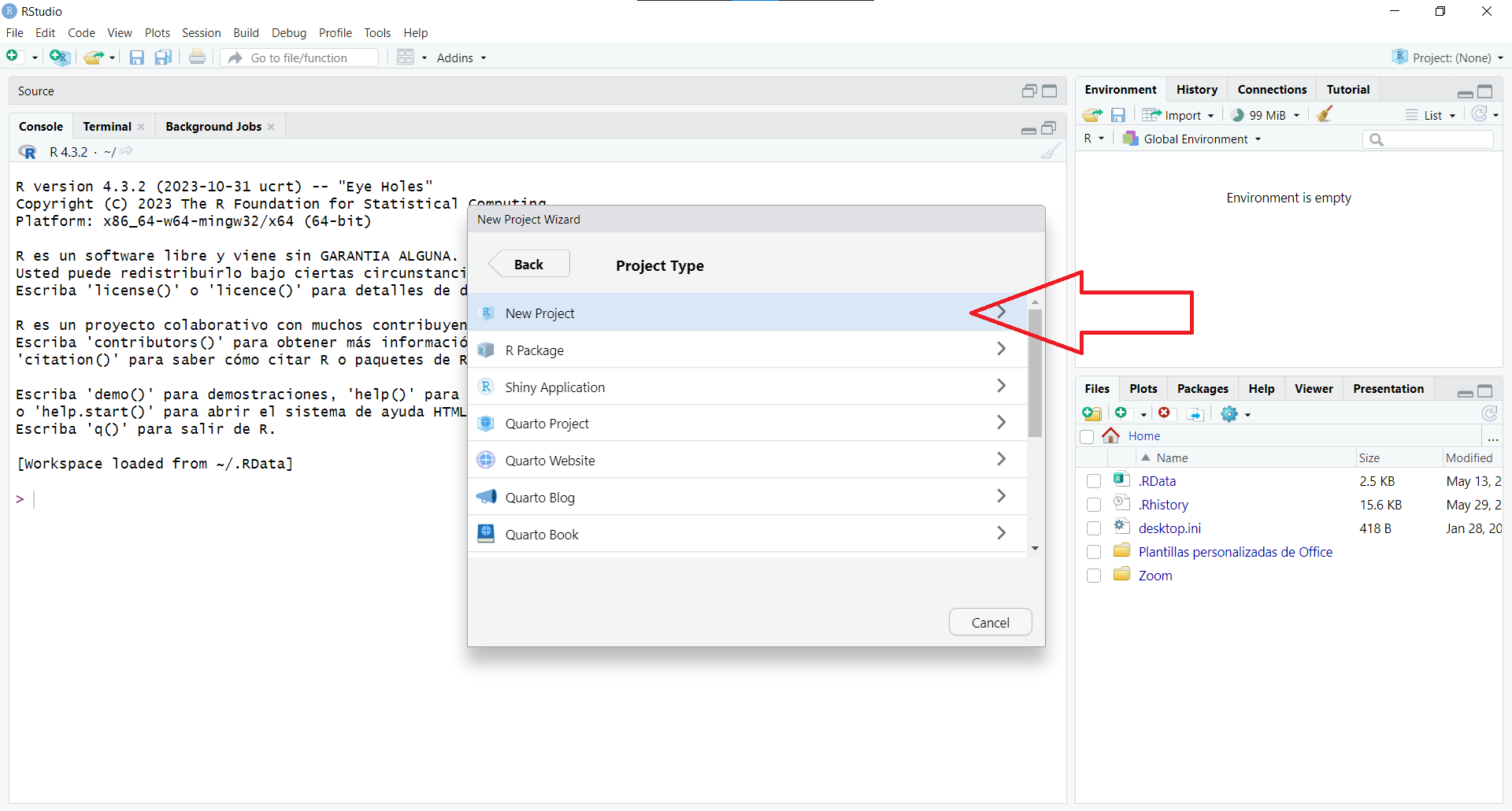
Seleccionar Archivo -> Nuevo proyecto
Como veremos en detalle en la próxima sesión, muchas de las funciones que utilizamos en R están contenidas en librerías o paquetes (packages).
La lógica de R es instalar librerías (solo 1 vez, con install.packages("librería")), y luego cargarlas cada vez que es necesario usarlas (con library(librería)). El problema de esto es que a veces no se sabe claramente qué librerías están instaladas y cuales no, lo que va a arrojar error al cargarlas. Y, como suele suceder en R, existe una librería para solucionar este problema que se llama pacman (package manager). Lo que hace pacman es cargar la librería, y si no está instalada, la instala y la carga:
Para utilizar la primera vez (si es que no está instalada):
Y en adelante, las librerías se cargan así: pacman::p_load(libreria1, libreria2, libreriaX)
Para esta sesión las librerías que vamos a utilizar son:
dplyr: ajuste general de datos
guaguas: paquete que contiene los datos de nombres de guaguas (bebés) registrados en Chile entre 1920 y 2021 según el Registro Civil e Identificación
ggplot2: para gráficos
Previo a la carga de nuestra base de datos, y posterior a la carga de librerías, se recomienda ejecutar los siguientes comandos:
rm(list=ls()) permite comenzar con un espacio de trabajo (environment) vacío y sin otros objetos.options(scipen=999) desactiva la notación científica, es decir, veremos los valores numéricos con todos sus decimales.Cargamos la base de datos desde el paquete (para otras bases de datos se deben importar de otra forma, esto es solo como ejemplo)
Conocemos las dimensiones de la base de datos:
Son 858782 casos y 5 variables.
Los nombres de estas variables son:
Y la base se ve así:
Ahora probemos algunas funciones para seguir explorando la base:
Podemos ver la cantidad de nombres “F” (femenino), “M” (masculino) e “I” (indefinido) inscritos entre 1920 y 2021.
Pueden buscar sus nombres y probar, utilizamos la funcion filter del paquete dplyr:
o:
# A tibble: 63 × 5
anio nombre sexo n proporcion
<dbl> <chr> <chr> <dbl> <dbl>
1 1931 Kevin M 1 0.0000120
2 1963 Kevin M 1 0.0000035
3 1964 Kevin M 1 0.00000344
4 1967 Kevin M 4 0.0000131
5 1970 Kevin M 6 0.0000210
6 1971 Kevin M 3 0.00000936
7 1972 Kevin M 3 0.00000945
8 1973 Kevin M 2 0.00000633
9 1974 Kevin M 5 0.0000163
10 1976 Kevin M 2 0.00000724
# ℹ 53 more rowsE incluso pueden ver la cantidad de personas con su nombre, en el mismo año que ustedes nacieron:
Avanzando un poco más, podemos utilizar ggplot2 para hacer un gráfico de líneas que muestre la evolución en el tiempo:
datos <- filter(base, nombre=="Kevin")
ggplot(datos, aes(x = anio, y = n)) +
geom_line() +
labs(x = "Año", y = "Número de personas", title = "Número de personas llamadas Kevin por año")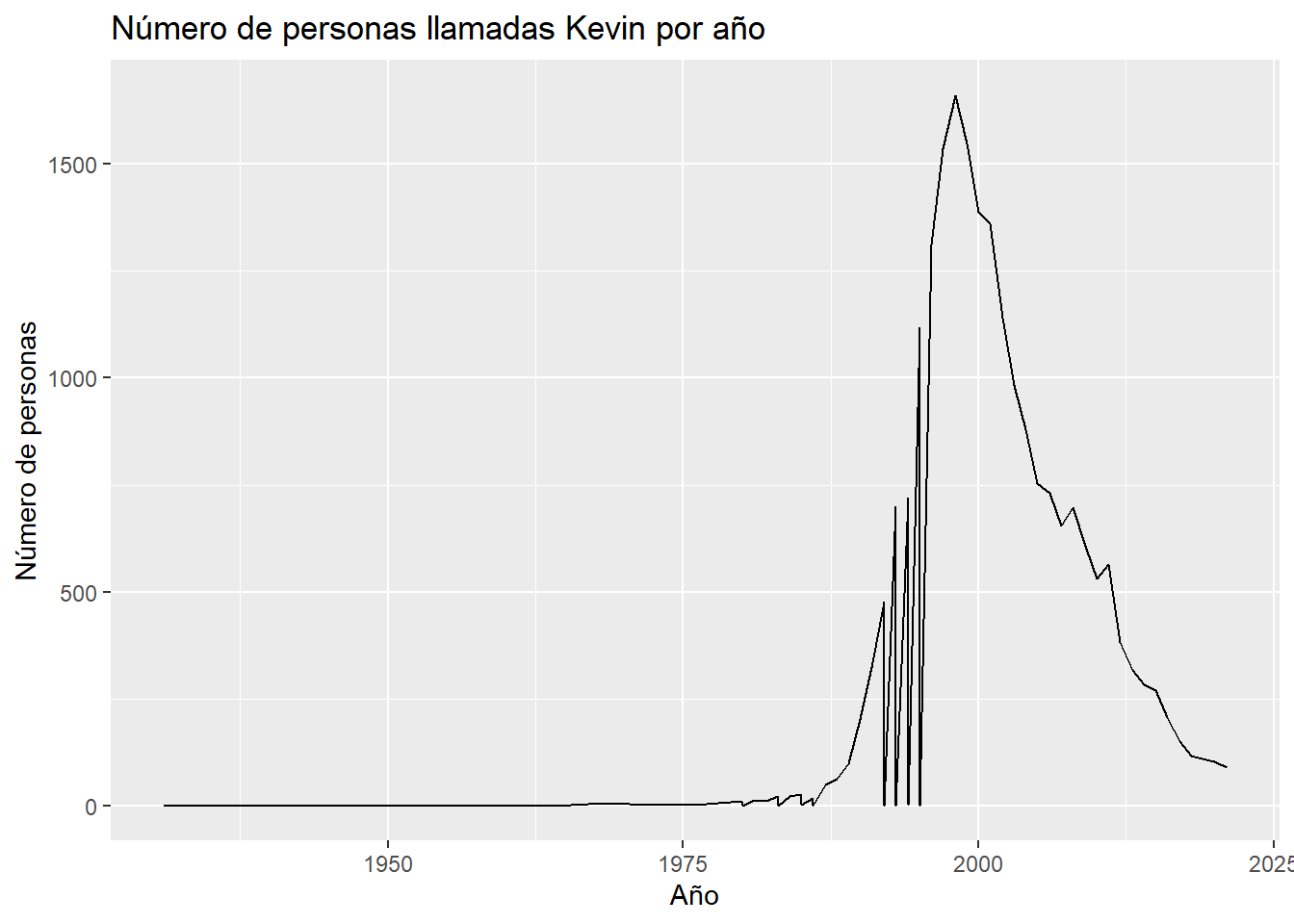
¿Qué puede explicar el peak de “Kevins” previo a los 2000?
spoiler: link